Ramlan explica su modelo de visualización de rejilla bacteriana y cómo encaja en el «más amplio».Condenar se basa en todo» tradición.
Aquí en Ars, hemos cubierto versiones de Condenar corriendo en todo desde impresoras pirateadas a notepad.exe de Windows a una versión que se ejecuta en el interior Condenar sí mismo. Pero estos y los otros muchos y variados ejemplos de extraños Condenar plataformas Todos carecen de la pura rareza biológica de un nuevo modelo para mostrar el juego usando una cuadrícula de E. coli bacterias.
estudiante de posgrado del MIT Lauren Ramlan describe un método para crear el quijotesco Condenar mostrar en «Píxeles de 1 bit codificados en E. coli para la visualización de medios digitales interactivos» el proyecto final de un Principios de la biología sintética clase. El proyecto de Ramlan se basa en investigaciones anteriores describiendo cómo el ADN en E. coli Las bacterias se pueden utilizar para codificar circuitos digitales completos y cómo se puede inducir a las bacterias a emitir fluorescencia como una forma tosca de pantalla digital.
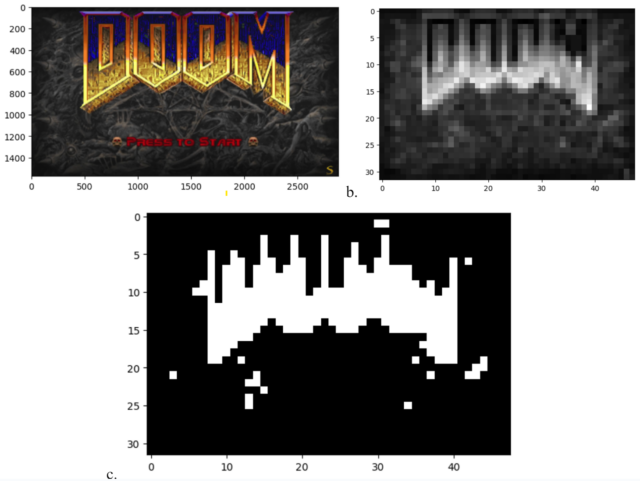
El artículo de Ramlan no se toma la enorme molestia de codificar todo Condenar para ejecutarse en ADN bacteriano, lo que el autor describe como «una hazaña gigantesca que ni siquiera puedo imaginar que se acerque». En cambio, el juego se ejecuta en una computadora estándar, con dispositivos aislados. E. coli células en una rejilla de micropocillos estándar de 32 × 48 sirviendo como una tosca pantalla de baja resolución.
Después de reducir cada cuadro del juego a un mapa de bits en blanco y negro de 32×48, Ramlan describe un sistema mediante el cual un controlador de pantalla utiliza un conocido par represor-operador químico para inducir a cada célula individual en la cuadrícula a expresar una proteína fluorescente o no. La red resultante de bacterias brillantes (que sólo se simula en el proyecto de Ramlan) puede considerarse técnicamente una muestra de Condenar jugabilidad, aunque la falta de sombreado uniforme en escala de grises hace que la imagen resultante sea bastante indescifrable, para ser honesto.
El tiempo necesario para que todo este proceso se realice también limita la utilidad de la visualización bacteriana teórica. Utilizando un modelo de Python, Ramlan calcula que se necesitarían 8 horas y 20 minutos para que brillara E. coli que la celda «regrese aproximadamente a su estado inicial», incluidos 70 minutos completos para «alcanzar la salida máxima de visualización» durante el ciclo. Eso se traduce en una velocidad de fotogramas de 0,00003 fps que duraría cinco horas. Condenar encontrarse con un trabajo de 599 años más apropiado para Lapsos de atención que la duración de la vida humana.
Todas esas advertencias se combinan para hacer de esta una de las adiciones más cargadas de tecnicismos a el siempre creciente «Condenar se ejecuta en todo» lista. Aún así, el esfuerzo muestra hasta dónde llegarán algunas personas para convertir cualquier cosa en una teoría teórica. Condenar-Pantalla lista. Como escribe Ramlan en su artículo: «Correr Condenartodo lo que uno necesita es una pantalla y fuerza de voluntad.»
Imagen de listado por porfkfkrErbe / Christopher Pooley