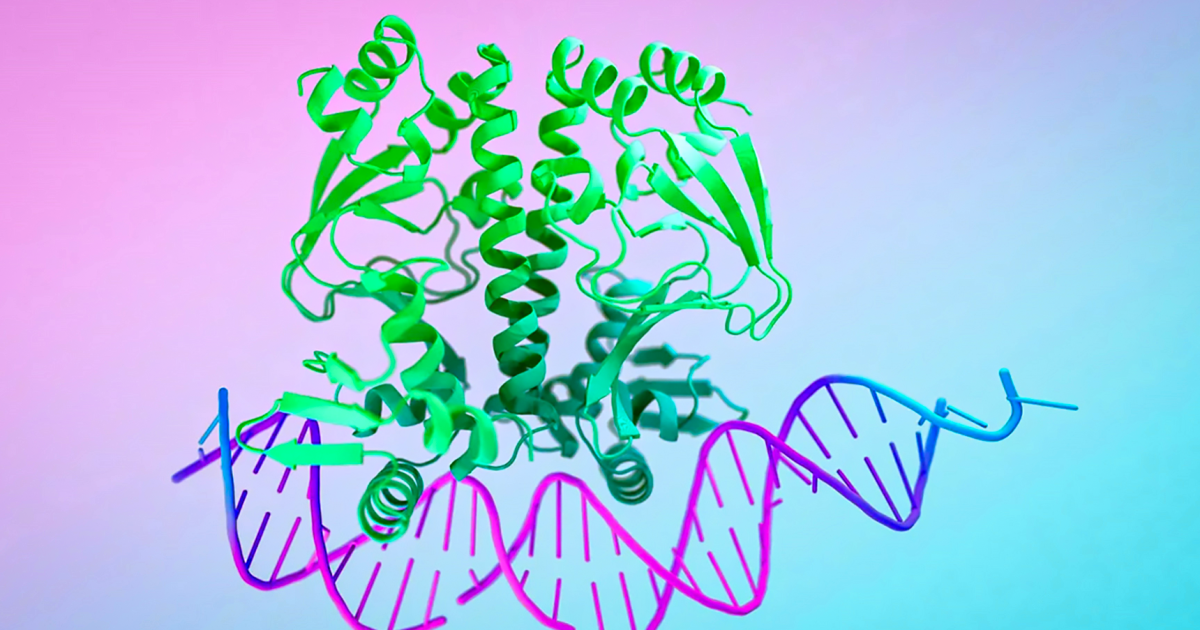
Las proteínas son uno de los inventos más increíbles y versátiles de la naturaleza. Estos componentes esenciales de la vida catalizan prácticamente todas las reacciones químicas del cuerpo, regulan la expresión genética y el sistema inmunológico, constituyen los elementos estructurales principales de todas las células y forman los componentes principales del músculo.
Pero ¿por qué esta IA se llama ‘AlphaFold’? Las proteínas son cadenas de aminoácidos que se pliegan espontáneamente para formar una estructura tridimensional crucial para la función biológica de la proteína. Puedes observar sus componentes y secuencias en papel, pero si no sabes en qué forma 3D se pliegan, no puedes predecir qué harán o cómo interactuarán con otras moléculas.
Se han utilizado varias técnicas experimentales operadas por humanos para determinar las estructuras de las proteínas, pero requieren mucho tiempo y son costosas. Teniendo en cuenta que hay más de 200 millones de proteínas conocidas en todas las formas de vida (y, hasta ahora, sólo se han identificado 170.000 estructuras proteicas), tenía sentido incorporar la IA para acelerar el proceso. Pero, hasta AlphaFold, los programas no habían podido predecir las estructuras de las proteínas de una manera tan precisa como las técnicas experimentales basadas en humanos.
AlphaFold 2, lanzado en 2021, fue un gran avance, predijo estructuras tridimensionales para casi todas las proteínas del cuerpo humano y permitió todo tipo de ciencia de vanguardia. En menos de tres años, ha sido utilizado por investigadores de todo el mundo para acelerar los descubrimientos en tratamiento para el cáncer, vacunas contra la malariala creacion de enzimas que comen plásticoy muchos otros – el Papel Alphafold 2 Actualmente enumera más de 14.000 citas.
Entonces, ¿en qué sentido es una mejora AlphaFold 3? Bueno, la versión más nueva va más allá de simplemente predecir la estructura y las interacciones de las proteínas para incluir todo, desde múltiples proteínas hasta ADN, ARN y ligandos de moléculas pequeñas. (La mayoría de los medicamentos son ligandos que se unen a proteínas para cambiar la forma en que interactúan en la salud y las enfermedades humanas).
Esto lo convierte en un recurso absolutamente sin precedentes para simular cómo proteínas específicas del cuerpo interactuarán con moléculas de fármacos específicas.

Google DeepMind/Laboratorios isomórficos
El GIF de arriba le da una idea de la estructura que genera AlphaFold 3. Muestra su predicción estructural para una proteína de pico (azul) de un virus del resfriado común mientras interactúa con anticuerpos (turquesa) y azúcares simples (amarillo). Puede ver con qué precisión el modelo de AlphaFold 3 coincide con la verdadera estructura de la proteína, que está subyacente en gris.
Para lograr estas capacidades avanzadas, AlphaFold 3 se entrenó con datos estructurales moleculares globales almacenados en el Banco de datos de proteínas. Deepmind dice que puede procesar más del 99% de todos los complejos biomoleculares conocidos en esa base de datos. Además, su módulo evoformerse mejoró la arquitectura que permitió a AlphaFold 2 funcionar como lo hacía.
Así es como funciona el sistema AlphaFold en muy, muy términos básicos. (Gracias al Grupo de Informática de Proteínas de la Universidad de Oxford por su explicación más fácil de entender.) Toma la secuencia de aminoácidos ingresada, busca en bases de datos secuencias similares ya identificadas en otros organismos vivos, extrae toda la información relevante usando un transformador (ese es el Evoformer) y pasa esa información a una red neuronal que produce un Estructura 3D: una larga lista de coordenadas que representan la posición de cada átomo de la proteína, incluidas las cadenas laterales.

Google DeepMind/Laboratorios isomórficos
Lo que hace el nuevo y mejorado Evoformer es ensamblar sus predicciones estructurales utilizando una red de difusión, como las que se encuentran en los generadores de imágenes de IA. Como señala la publicación conjunta del blog de Mente profunda y Laboratorios isomórficos Como explica el anuncio de AlphaFold 3, «comienza con una nube de átomos y, a lo largo de muchos pasos, converge en su estructura molecular final y más precisa».
En una entrevista reciente con BloombergTom Mackenzie, director ejecutivo y cofundador de Google DeepMind (y director ejecutivo y fundador de Isomorphic Labs), Demis Hassabis, analizó las implicaciones del uso de AlphaFold 3 en el descubrimiento de fármacos.
«El santo grial del descubrimiento de fármacos no es sólo conocer la estructura de la proteína, que es lo que hizo AlphaFold 2, sino también diseñar compuestos farmacológicos llamados ligandos que se unen a la superficie de la proteína», dijo Hassabis. “Y usted quiere saber dónde se une y con qué fuerza se une para poder diseñar el tipo correcto de compuesto farmacológico. Por lo tanto, AlphaFold 3 es un gran paso en esa dirección de predecir la unión proteína-ligando y cómo funcionará esa interacción”.
En enero de este año, Isomorphic Labs Anunciado una asociación estratégica con los gigantes farmacéuticos Eli Lilly y Novartis, por un valor combinado de alrededor de 3 mil millones de dólares. Pero lo que es increíble aquí es el cronograma de producción de medicamentos que se espera que resulte de estas asociaciones.
«Así que ya estamos trabajando en programas de drogas reales», dijo Hassabis. «Y esperaría que tal vez en los próximos años aparezcan los primeros medicamentos diseñados con IA. [appearing] en la clinica.»
«Si me preguntas qué es lo primero que la IA podría hacer por la humanidad», continuó, «sería resolver, ya sabes, cientos de enfermedades terribles. No puedo imaginar un mejor caso de uso para la IA. Así que esa es en parte la La motivación detrás de Isomorphic y AlphaFold y todo el trabajo que hacemos en ciencia es hacer avanzar a la sociedad en estos grandes aspectos».
La entrevista completa entre Hassabis y Mackenzie se puede ver en el vídeo a continuación.
CEO de Google DeepMind sobre descubrimiento de fármacos, exageración, isomórfico
Cuando se probó, AlphaFold 3 demostró una precisión de vanguardia en la predicción de interacciones similares a medicamentos, incluidas proteínas unidas a ligandos y anticuerpos unidos a proteínas diana.
Utilizando el punto de referencia PoseBusters, se descubrió que era un 50% más preciso que los mejores métodos existentes, sin necesidad de ingresar ninguna información estructural. PoseBusters comprueba la plausibilidad química y física de las «poses» moleculares y de ligandos proteicos generadas por un modelo de aprendizaje profundo.
Y puedes jugar con él tú mismo. AlphaFold 3 está disponible a través de Servidor AlphaFold, que incluye una base de datos de 200 millones de estructuras de proteínas. Este fantástico recurso es gratuito para los científicos que realizan investigaciones no comerciales o, incluso, simplemente para los usuarios curiosos de la Web en todo el mundo.
Demostración del servidor AlphaFold – Google DeepMind
Predecir las estructuras de las proteínas sin una herramienta como esta puede llevar… Bueno, aproximadamente el mismo tiempo que lleva completar un doctorado, y puede costar cientos de miles de dólares. Muy parecido a como La herramienta GNoME de DeepMind ha catapultado el descubrimiento de materiales y cristales cientos de años hacia el futuroAlphaFold 3 promete acelerar radicalmente vastas áreas de las ciencias biológicas y farmacéuticas.
«Esta nueva ventana a las moléculas de la vida revela cómo están conectadas y ayuda a comprender cómo esas conexiones afectan las funciones biológicas, como las acciones de los medicamentos, la producción de hormonas y el proceso de reparación del ADN que preserva la salud», dijo Google. Laboratorios DeepMind e Isomórficos. «Este salto podría desbloquear una ciencia más transformadora, desde el desarrollo de materiales biorrenovables y cultivos más resistentes hasta la aceleración del diseño de fármacos y la investigación genómica».
No podemos esperar a ver adónde nos lleva esta tecnología.
La investigación sobre las capacidades predictivas de AlphaFold 3 se publicó en Naturaleza.
Fuentes: Google DeepMind, Laboratorios isomórficos